Гаплогруппа R1 (Y-ДНК)
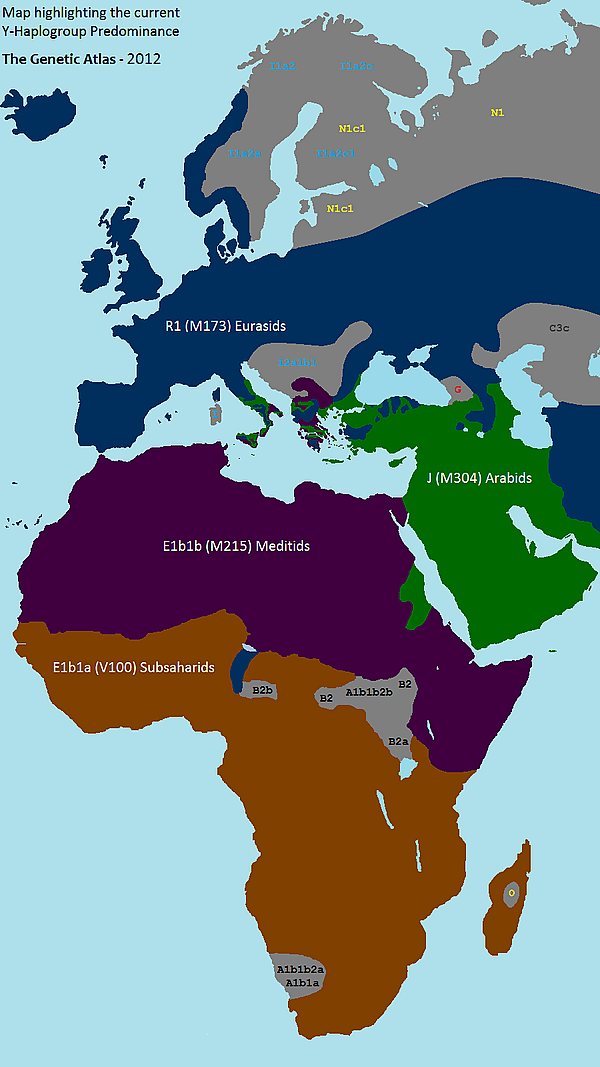
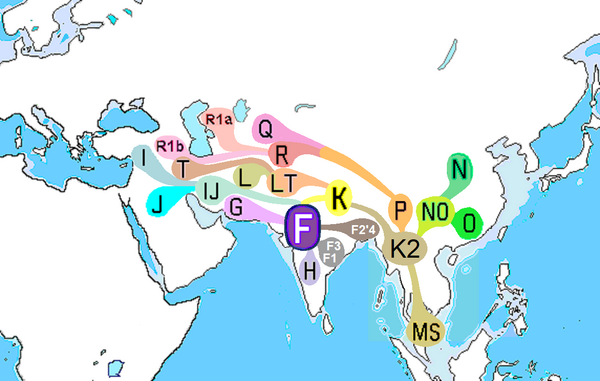
Гаплогруппа R1 — наиболее распространенная подгруппа Гаплогруппы R, отмеченная мутацией M173. Её два основных субклада R1a (M17) и R1b (M343) (прочие варианты встречаются исключительно редко) являются наиболее распространёнными во всей Европе и западной Азии. Это связано с переселениями после последнего ледникового максимума.
Что важно знать
Происхождение
Происходит от мутации гаплогруппы R, произошедшей у мужчины, жившего на территории Южной Сибири[3][2][4][5] (исходя из распространения линий R2 и R*), ок. 28 200 лет назад. Последний общий предок современных носителей гаплогруппы R1 жил 22 800 лет назад (даты определены по снипам компанией YFull[6]).
Субклады
Гаплогруппа R1a (M17), предположительно, зародилась в Южной Сибири ок. 22 800 лет назад (дата определена по снипам компанией YFull[1]). Встречается от Исландии до Индии, современный центр гаплогруппы находится на территории Польши. Эта гаплогруппа стала маркером распространения протоиндоевропейских народов. Экспансия индоевропейцев способствовала миграции гаплогруппы R1a в Иран и в Индию.
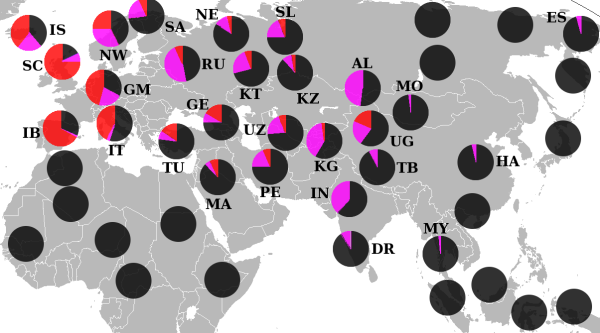
Наибольшее распространение имеет в Восточной Европе: среди лужичан (63,39 %), поляков (ок. 56 %), украинцев (ок. 47 %), русских (52 %), белорусов (49 %), башкир (26 %) (у башкир Саратовской и Самарской обл. до 48 %)[7], татар (38 %); и в Центральной Азии: у хотонов (82.5 %)[8], киргизов (63 %)[9], таджиков из Пенджикента (68 %), хазарейцев из Пакистана (60,1 %)[10], шорцев (58,8 %)[11], юг-алтайцев (58,1 %)[12], телеутов (55,3 %)[11], уйгуров (около 30%) [13], узбеков (до 28,1%)[14]. Умеренное распространение в Скандинавских странах (23 % в Исландии, 18-22 % в Швеции и Норвегии), в Иране (25 %?).
У брахманов индийских штатов Западная Бенгалия и Уттар-Прадеш данная гаплогруппа встречается с частотой 72 % и 67 % соответственно[15].
Примечания
Литература
- Behar et al. (2003), Multiple Origins of Ashkenazi Levites: Y Chromosome Evidence for Both Near Eastern and European Ancestries, Am. J. Hum. Genet. Т. 73: 768–779, PMID 13680527, <http://www.journals.uchicago.edu/AJHG/journal/issues/v73n4/40097/40097.html>. Also at http://www.ucl.ac.uk/tcga/tcgapdf/Behar-AJHG-03.pdf
- Luigi Luca Cavalli-Sforza. The History and Geography of Human Genes (неопр.). — Princeton University Press, 1994. — ISBN 0-691-08750-4.
- Cinnioğlu et al. (2004), Excavating Y-chromosome haplotype strata in Anatolia, Hum Genet Т. 114: 127, doi:10.1007/s00439-003-1031-4, <http://www.springerlink.com/content/q884mpdr929yuye0/fulltext.pdf> (недоступная ссылка)
- Passarino et al. (2002), Different genetic components in the Norwegian population revealed by the analysis of mtDNA and Y chromosome polymorphisms, Eur. J. Hum. Genet. Т. 10 (9): 521–9, PMID 12173029, <http://www.nature.com/ejhg/journal/v10/n9/full/5200834a.html>.
- Saha et al. (2005), Genetic affinity among five different population groups in India reflecting a Y-chromosome gene flow, J. Hum. Genet. Т. 50 (1): 49–51, PMID 15611834, DOI 10.1007/s10038-004-0219-3.
- Semino et al. (2000), The Genetic Legacy of Paleolithic Homo sapiens sapiens in Extant Europeans, Science Т. 290, <http://hpgl.stanford.edu/publications/Science_2000_v290_p1155.pdf>. Проверено 28 апреля 2010. Архивная копия от 25 ноября 2003 на Wayback Machine.
- Sengupta et al. (2005), Polarity and Temporality of High-Resolution Y-Chromosome Distributions in India Identify Both Indigenous and Exogenous Expansions and Reveal Minor Genetic Influence of Central Asian Pastoralists, Am. J. Hum. Genet. Т. 78 (2): 202–21, PMID 16400607, doi:10.1086/499411, <http://www.pubmedcentral.nih.gov/articlerender.fcgi?artid=1380230>.
- Soares et al. (2010), The Archaeogenetics of Europe, Current Biology Т. 20, doi:10.1016/j.cub.2009.11.054, <http://download.cell.com/current-biology/pdf/PIIS0960982209020697.pdf?intermediate=true>. Проверено 28 апреля 2010. Архивная копия от 8 июля 2011 на Wayback Machine
- Wells et al. (2001), The Eurasian Heartland: A continental perspective on Y-chromosome diversity, Proc. Natl. Acad. Sci. U. S. A. Т. 98 (18): 10244–9, PMID 11526236, doi:10.1073/pnas.171305098, <http://www.pnas.org/cgi/content/full/98/18/10244>. Also [1]